搜索结果: 31-45 共查到“作物学 全基因组”相关记录66条 . 查询时间(0.896 秒)
雷蒙德氏棉MAPKKK基因家族全基因组筛选及其同源基因在陆地棉中表达分析
雷蒙德氏棉 全基因组筛选 MAPKKK基因家族 芯片数据分析
<
2020/4/27
【目的】丝裂原活化蛋白质激酶激酶激酶(Mitogen-activated protein kinase kinase kinase,MAPKKK)家族在植物的胁迫反应和发育过程中起重要调控作用。本研究旨在筛选雷蒙德氏棉MAPKKK基因并分析其功能。【方法】以已鉴定的拟南芥MAPKKK蛋白序列为种子序列,在已发表的雷蒙德氏棉全基因组数据库中,通过本地BLAST以及Pfam和SMART鉴定雷蒙德氏棉M...
2019年5月1日,福建农林大学教授庄伟建,联合印度国际半干旱热带作物研究所、华北理工大学等23个研究机构的研究成果“栽培种花生基因组揭示了豆科植物的核型、多倍体进化和作物驯化在《自然・遗传学》在线发表。该项研究在全世界范围内首次破译了四倍体栽培种花生的全基因组,标志着我国在栽培种花生基因组、花生染色体起源、花生及豆科主要类群核型演化、花生基因组结构变异、花生物种起源与分子育种研究方面处于国际领先...
科学家成功解读硬粒小麦全基因组图谱
科学家 硬粒小麦 全基因组 图谱
<
2019/4/19
近日,来自意大利、加拿大、德国等多国科研机构的科学家共同在Nature Genetics上发表了题为“Durum wheat genome highlights past domestication signatures and future improvement targets”的文章,绘制并解读了硬粒小麦(durum wheat)的全基因组图谱,这对于比较和挖掘小麦祖先中的优异等位基因具有重...
全基因组关联分析在作物育种研究中的应用
全基因组关联分析(GWAS) 连锁不平衡(LD) 作物分子标记辅助育种
<
2020/3/9
全基因组关联分析(GWAS)是一种针对全基因组范围内的遗传变异进行基因分型,寻找某一群体内性状与分子标记或候选基因间关系的分析方法。GWAS对于连锁标记开发、目的基因挖掘和复杂性状的遗传研究具有重要作用,在作物数量性状研究和作物育种中得到了广泛的应用。本文简要综述了利用GWAS挖掘与作物重要性状关联基因的研究过程中,群体结构、群体数量、连锁不平衡(LD)等因素对GWAS的影响,并重点分析了GWAS...
【目的】谷胱甘肽还原酶基因(Glutathione reductase gene,GR)家族参与植物生长发育和非生物胁迫响应等生物进程,但其在棉花中的特性及功能尚不清楚。本研究通过在异源四倍体陆地棉(Gossypium hirsutum)、海岛棉(G. barbadense)及其可能的二倍体祖先种亚洲棉(G. arboreum)和雷蒙德氏棉(G. raimondii)中对GR基因家族全基因组鉴定与...
中国科学家率先完成四倍体花生栽培种全基因组测序
花生遗传改良 花生产业
<
2017/12/25
花生是世界上重要的油料作物和第二大植物蛋白质来源。中国花生在单产、总产和消费量均居世界首位。花生栽培种为异源四倍体植物,基因组大、重复序列比例高,组装难度大,全基因组测序一直未能突破,严重影响了花生研究和应用。
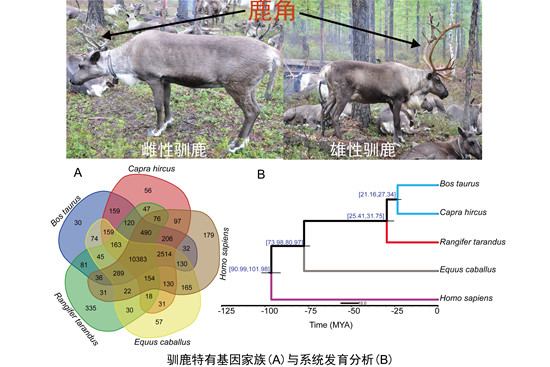
中国农业科学院特产研究所首次破译鹿科动物全基因组序列(图)
中国农业科学院特产研究所 鹿科动物 全基因组序列
<
2017/11/8
近日,由中国农业科学院特产研究所李光玉研究员带领创新团队在国际上首次破译鹿科动物全基因组序列。驯鹿全基因组测序的完成,不仅为研究人员从基因组水平挖掘驯鹿生长、代谢和抗寒等重要性状的分子机制提供了科学指导,而且为驯鹿驯化历史、基因组演化、群体遗传及鹿类动物的进化等理论研究奠定了重要基础。相关研究成果于11月1日在线发表在《GigaScience》上。
WRKY转录因子是一类植物响应生物、非生物胁迫,对生长发育都起重要调控作用的转录因子。在甜菜全基因组信息分析的基础上,鉴定WRKY家族基因(BvWRKYs),解析其组织特异性及盐、热胁迫下的表达情况,为该类基因的功能研究提供参考,为观赏甜菜和石竹目其他观赏植物的基因工程打下基础。【方法】以75条拟南芥WRKY蛋白为参考,根据WRKY保守蛋白序列(PF03106)利用hmm和BLAST同源性搜索对甜...
美国科学家开发全基因组测序水稻变体
全基因组 水稻变体
<
2017/8/16
水稻不仅是全球一半人口的主食,也为研究能源作物提供了模型。为优化生物燃料作物,科学家正寻找决定水稻产量、抗病性和灌溉效率等性状的基因。最近在《植物细胞》杂志刊登的一篇论文中,美国加州大学戴维斯分校的研究团队与来自能源部联合基因组研究所的合作者,宣布开发出粳稻Kitaake的第一个全基因组测序快中子诱导突变体种群,一种新型的短生命周期水稻品种模型。
甘蓝型油菜polCMS育性恢复位点的全基因组关联分析
甘蓝型油菜 波里马细胞质雄性不育 育性恢复基因 全基因组关联分析 SNP
<
2017/11/17
甘蓝型油菜波里马细胞质雄性不育(pol CMS)在中国已被广泛应用于杂交种育种,其育性恢复程度表现出受1对主效基因的控制,并受微效修饰基因的影响。通过全基因组关联分析方法挖掘育性恢复位点,并对候选基因进行比较分析。【方法】通过芸薹属60K SNP芯片对308份甘蓝型油菜自然群体进行基因型分型,并用pol CMS系301A作母本,与上述材料分别进行杂交得到308份F1,每份F1分别于2013年和20...

2017年3月7日,《自然•遗传学》(Nature Genetics)在线发表了我校张献龙教授领导的棉花团队的最新研究成果:“棉花驯化过程中的不对称亚基因组选择和顺式调控分歧”(Asymmetric subgenome selection and cis-regulatory divergence during cotton domestication)。这项研究不仅首次提出了棉花纤维...
解析甘蓝型油菜发芽期根和下胚轴发育及耐盐性的调控位点,筛选油菜耐盐性相关的候选基因,可为油菜耐盐性改良提供依据。【方法】以317份具有代表性的甘蓝型油菜自交系为材料,在正常生长和盐胁迫条件下进行沙培鉴定,利用芸薹属60K SNP芯片和全基因组关联分析鉴定正常生长与盐胁迫下甘蓝型油菜发芽期根和下胚轴长度显著关联的SNP,并确定其连锁不平衡区间。通过区间内基因的功能注释及盐胁迫下油菜幼苗根和叶片转录组...
芝麻大规模全基因组关联分析完成
芝麻 大规模全基因组关联
<
2015/10/22
由中国农业科学院油料作物研究所张秀荣研究员领衔的芝麻与特色油料遗传育种创新团队,与中国科学院国家基因研究中心等单位合作,在国际上率先完成了芝麻高密度单倍型图谱构建、主要农艺性状大规模全基因组关联分析。2015年10月19日,国际知名期刊《自然・通讯》杂志在线发表了上述研究成果。

中国农业科学院油料作物研究所率先完成芝麻全基因组关联分析(图)
中国农业科学院油料作物研究所 芝麻全基因组关联分析
<
2015/10/20
近日,从中国农业科学院油料作物研究所获悉,张秀荣研究员领衔的芝麻与特色油料遗传育种创新团队与中国科学院合作,在国际上率先完成了芝麻高密度单倍型图谱构建和主要农艺性状大规模的全基因组关联分析,发掘了一批关联位点和候选基因。相关研究成果于2015年10月19日在线发表在国际知名期刊《自然通讯(Nature Communications)》杂志上。